Frühe MRT-Untersuchungen sind entscheidend für Patient:innen, die sich einer Hirntumorresektion unterzogen haben, um den Erfolg der Operation zu beurteilen und weitere Therapieschritte zu planen. Allerdings führt intrakranielle Luft häufig zu „Artefakten“ oder Bildverzerrungen, die die Befundung erschweren.
In einer kürzlich im European Journal of Radiology veröffentlichten Studie untersuchen Christer Ruff et al. eine robustere Bildgebungstechnik zur Lösung dieses Problems.
Die Herausforderung: Hindernisse in der postoperativen Bildgebung
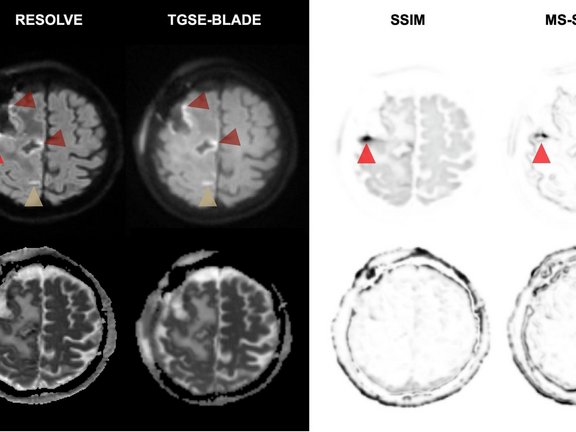
Die diffusionsgewichtete Bildgebung (DWI) ist essenziell zur Identifizierung perioperativer ischämischer Veränderungen (kleine Schlaganfälle oder Gewebeschädigungen) in der Nähe des Resektionsgebiets. Standardtechniken wie RESOLVE DWI sind häufig durch geometrische Verzerrungen und Suszeptibilitätsartefakte beeinträchtigt, die durch Luft-Gewebe-Grenzflächen nach der Operation entstehen. Diese Verzerrungen erschweren die Interpretation zwischen Artefakten, ischämischen Veränderungen und postoperativen Veränderungen.
Die Studie: Vergleich von TGSE-BLADE und RESOLVE
Die Forschenden führten eine retrospektive Studie mit 33 Patient:innen durch, die innerhalb von 48 Stunden nach einer Hirntumorresektion eine 1,5-Tesla-MRT erhielten. Verglichen wurden zwei fortgeschrittene Techniken:
- RESOLVE DWI: Eine gängige Technik, bei der die Datenerfassung segmentiert wird, um bestimmte Verzerrungen zu reduzieren.
- TGSE-BLADE DWI: Eine Nicht-EPI-Technik mit „radialer“ Datenerfassung, die unempfindlich gegenüber Magnetfeldinhomogenitäten ist.
mint Lesion, eine Softwarelösung für eine standardisierte und computergestützte Auswertung von radiologischen und klinischen Daten, wurde eingesetzt, um bidimensionale Messungen des Resektionsdefekts in verschiedenen Bildsequenzen durchzuführen.
Durch den Vergleich dieser Messungen mit standardisierten T1-gewichteten Referenzbildern konnte objektiv quantifiziert werden, welche DWI-Technik die genaueste und verzerrungsärmste Darstellung des Operationsgebiets lieferte.
Zentrale Ergebnisse
Die Studie zeigt, dass TGSE-BLADE DWI RESOLVE in mehreren entscheidenden Punkten überlegen war:
- Reduzierte Verzerrung: TGSE-BLADE zeigte signifikant weniger geometrische Verzerrungen und Artefakte im Bereich der Resektion als RESOLVE (p < 0,001).
- Höhere Genauigkeit: Die Messungen des Resektionsareals in TGSE-BLADE-Bildern stimmten eng mit den T1-gewichteten Referenzaufnahmen überein, während RESOLVE aufgrund von Bildverzerrungen signifikante Abweichungen aufwies.
- Diagnostische Sicherheit: Neuroradiolog:innen berichteten über eine signifikant höhere diagnostische Sicherheit und eine bessere Gesamtbildqualität bei Verwendung von TGSE-BLADE.
- Abwägungen: Obwohl RESOLVE DWI ein leicht höheres Signal-Rausch-Verhältnis (SNR) aufwies, machte die Klarheit und Verzerrungsfreiheit von TGSE-BLADE diese Technik zum überlegenen Instrument für die klinische Beurteilung.
Fazit: Ein möglicher neuer Standard für die postoperative Versorgung
Die Studie kommt zu dem Schluss, dass TGSE-BLADE DWI eine robuste Alternative zu konventionellen Sequenzen in der postoperativen Hirnbildgebung darstellt. Durch die Minimierung von Artefakten infolge intrakranieller Luft ermöglicht die Technik eine klare Unterscheidung zwischen erwarteten postoperativen Veränderungen und tatsächlichen ischämischen Hirnschädigungen. Dies führt zu präziseren Verlaufskontrollen und einer verbesserten langfristigen Patientenversorgung.
Lesen Sie die Originalpublikation hier.
Christer Ruff, Till-Karsten Hauser, Paula Bombach, Daniel Vogl, Constantin Roder, Frank Paulsen, Deborah Staber, Vivien Richter, Leonie Zerweck, Ulrike Ernemann, Georg Gohla. “A comprehensive quantitative and qualitative assessment of TGSE-BLADE DWI in postoperative imaging following intracranial tumor resection.” European Journal of Radiology, Volume 196, 2026, ttps://doi.org/10.1016/j.ejrad.2026.112659.
![[Translate to German:]](/fileadmin/_processed_/6/e/csm_mintLesion33_b_7ad9795678.png)
![[Translate to German:]](/fileadmin/_processed_/9/f/csm_iRECIST-2016_c2779a7e10.png)
![[Translate to German:]](/fileadmin/_processed_/8/3/csm_mint_data_f4223f1a8c.png)